研究紹介 > 刊行物 > 研究成果選集 > 平成13年度 研究成果選集 2001 > スギの遺伝子地図とその利用
更新日:2012年7月18日
ここから本文です。
スギの遺伝子地図とその利用
| 森林遺伝研究領域 | ゲノム解析研究室 | 津村 義彦、谷 尚樹、伊原 徳子、松本 麻子、吉村 研介 |
| 生態遺伝研究室 | 吉丸 博志 | |
| 中央農業総合研究センター | 岩田 洋佳 | |
| 静岡大学 | 向井 譲 | |
| 元森林総合研究所職員 | 村井 正文 | |
| 森林遺伝研究領域長 | 長坂 壽俊 | |
背景と目的
樹木は農作物に比べて長い世代サイクルを持ち、選抜や検定に長期を要するため、育種年限の大幅な短縮や、森林の合理的な保全方法の確立が求められている。それには遺伝子技術や遺伝情報を活用した新たなバイオ技術の開発が不可欠であり、林木のゲノム解析研究はこれらの課題を解決する基盤的研究である。
スギは日本固有の最も重要な造林樹種である。本研究は、ゲノム解析のための目印となるDNA多型マーカーの開発を通して、スギの遺伝子地図(様々な形質を決める遺伝子の染色体における存在位置を表す)作製のために遺伝子の並びを調べる連鎖解析を行い、高密度な基盤遺伝子地図の構築を主要な目的としている。遺伝子の塩基配列を調べたり染色体上での遺伝子の並びを調べることにより、遺伝子を目印とした、いわゆるDNAマーカーを作ることができる。これらのDNAマーカーを用いることで優良なスギを直接選ぶことができ、林業の生産性向上への貢献、花粉症等の諸問題の解決、失われつつある森林資源の効果的な遺伝的管理手法の構築に向けた前進が図られ、わが国の林業の活性化への貢献が期待される。
成果
1. cDNAの塩基配列と簡便な共優性DNAマーカーの作出
スギゲノムではこれまでに実生、内樹皮、雄花、雌花、花粉由来の発現している遺伝子群であるcDNAライブラリーから約8,000の部分塩基配列情報を得た。これらのシークエンス情報からDNAの特定領域を数百万倍に増幅するPCR法を活用した共優性DNAマーカー(遺伝子のタイプがホモ接合型かヘテロ接合型かを見分けることができるマーカー)を合計で496個について開発した。スギで開発した遺伝子部分を特異的にPCR増幅するSTSマーカーをヒノキに応用し、約1/3のスギSTSマーカーが直接利用できることができた。またこれから64のヒノキのDNA多型マーカーを開発した。
2. 高密度遺伝子連鎖地図の作製
開発したDNAマーカーを用いて、遺伝子の地図を表す連鎖地図の構築を3家系を用いて行ってきた。そのうちのYA家系では遺伝子の集まりである連鎖群が基本染色体数に対応する11群に収束した。YA家系とクモトオシ×オキノヤマスギF2家系の連鎖地図の統合を行い、高密度基盤連鎖地図を構築した(図1)。ヒノキで開発したCAPSマーカーを用いてヒノキ連鎖地図の構築を行い、部分的ではあるが地図の構築ができている。有用形質である量的形質遺伝子座(QTL)のマッピングをクモトオシ×オキノヤマスギF2家系で行い、雄花と雌花の着花性、成長及び発根性のQTLのマッピングができた。
3 連鎖地図ベースのスギ遺伝子資源の評価
遺伝子資源の評価として全国から収集したスギは25集団で合計711個体である。これらを連鎖地図上にマップした共優性DNAマーカー120遺伝子座について解析を行った。その結果、日本海側と太平洋側の集団に大きく2分され、これまで形態的特徴からいわれてきたウラスギ系、オモテスギ系の2系統がゲノム上も分化していることを示唆していた(図2)。遺伝的変異性は西日本の集団が東日本に比べ高く、花粉分析による結果を支持するものであった。さらに分布の端の集団では高い連鎖不平衡を示した。これらの結果、遺伝資源の特性に則した管理が重要となる。
なお、本研究は「生物系特定産業技術研究推進機構プロジェクト」による。

図1 スギの基盤連鎖地図
433遺伝子座(172 CAPS遺伝子座、 22 RAPD遺伝子座、200 RFLP遺伝子座、1形態遺伝子座、37SSR遺伝子座) 、総地図距離1351.5 cM、平均遺伝子座間距離3.1 cM、矢印はスギのアレルゲンの主要遺伝子であるCryj1とCryj2を示す。
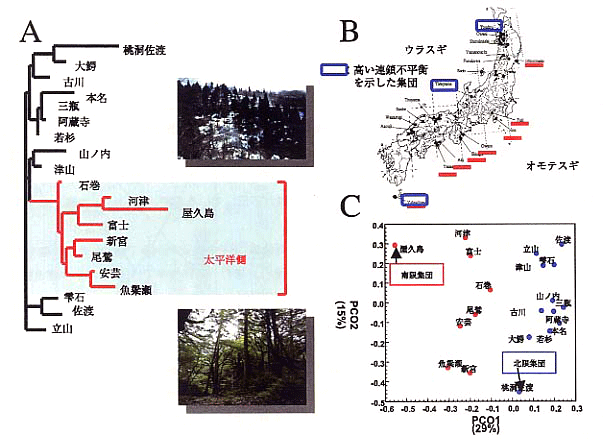
図2 スギの連鎖地図ベースでの遺伝資源の評価
A:120遺伝子座の分析にもとづく集団の遺伝的な関係を示す系統樹、枝の長さが遺伝的な近縁性を示す、
B:スギの天然分布と分析集団、C:主座標分析の結果、ウラスギとオモテスギが遺伝的に分化していた。
お問い合わせ
Copyright © Forest Research and Management Organization. All rights reserved.
